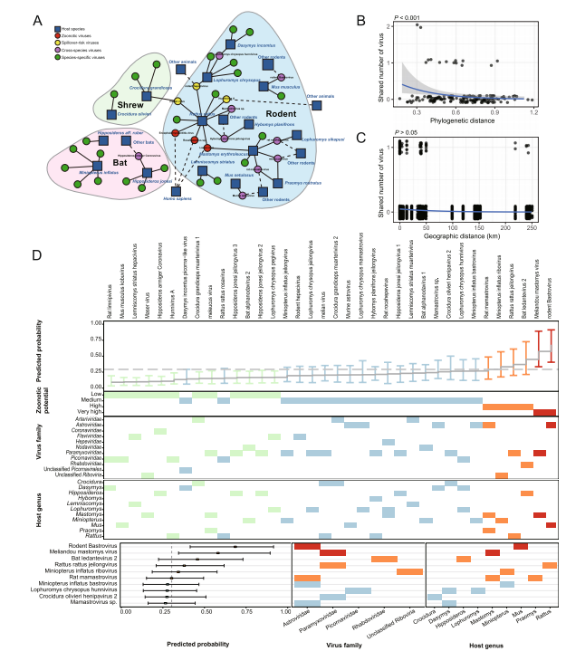
Eng rezent Studie, déi amMikrobiomhuet viral metagenomesch Analysen op 846 wëlle klenge Säugetieren - dorënner Fliedermais, Nager a Spëtzmais - duerchgefouert, déi a Sierra Leone a Westafrika gesammelt goufen. D'Studie huet insgesamt 39 Säugetieren-assoziéiert RNA-Viren identifizéiert, dorënner 26 nei an 13 virdru bekannt Viren. Ënnert dësen huet d'Famill Paramyxoviridae déi héchst Diversitéit opgewisen, während Nager déi gréisst Zuel vu virale Spezies haten (n = 26).
D'Bewäertung vum zoonotische Risiko huet dräi bekannt zoonotesch Virussen - Encephalomyokarditvirus, Lassavirus a Rocahepevirus sp. - souwéi dräi Virussen mat engem potenziellen Spillover-Risiko opgedeckt: Melianvirus, Nagetier-Hepatitisvirus an Hunnivirus A. Bemierkenswäert ass, datt ënner den nei identifizéierte Virussen de Bat ledantevirus 2 déi nootste phylogenetesch Verwandtschaft mam mënschlechen infizéierte Le Dantec-Virus gewisen huet. Serologesch Analysen hunn weider neutraliséierend Antikörper géint dëse Virus bei 2,8% vun den Awunner festgestallt, wat op eng fréier, wahrscheinlech onentdeckt, mënschlech Belaaschtung hiweist.
Dës Erkenntnisser ënnersträichen d'Präsenz vun engem wesentleche Viralreservoir, deen duerch Nagetieren dominéiert gëtt, a Westafrika a betount déi kritesch Wichtegkeet vun integréierten Iwwerwaachungsstrategien op der Grenzfläche tëscht Mënsch an Déier. D'Kombinatioun vu metagenomesche Screening mat serologescher Validatioun bitt e robuste Kader fir d'Identifikatioun vu Viren mat zoonoteschem a Spillover-Potenzial.

An de leschten zéng Joer stamen iwwer 60% vun den opkomende Infektiounskrankheeten beim Mënsch aus Déierereservoiren, woubäi Fliedermais, Nager a Spëtzmausen als Schlësselwierder vu zoonotesche Virussen unerkannt ginn. Afrika gëtt allgemeng als Hotspot fir zoonotesch Krankheeten ugesinn. Zum Beispill huet Sierra Leone iwwer 28.000 Fäll während dem Ebola-Ausbroch vun 2014-2016 gemellt.
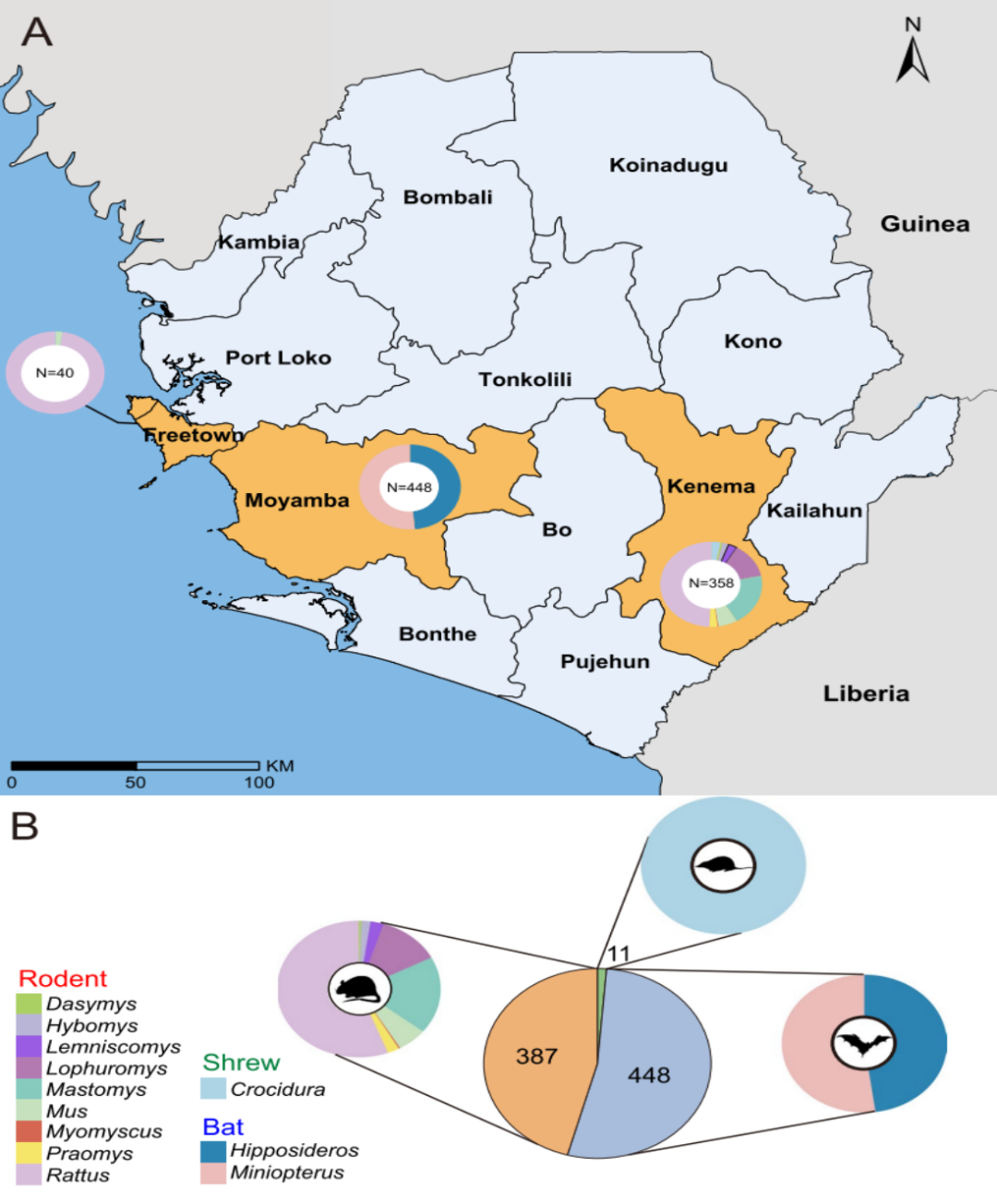
Trotz der bedeitender Belaaschtung vu zoonotesche Krankheeten an dëser Regioun, bleift d'Diversitéit an d'Verdeelung vu Viren bei wëlle klenge Mamendéieren net genuch charakteriséiert. Fir dës Lück ze schléissen, hunn d'Fuerscher eng systematesch Viromanalyse vun 846 wëlle klenge Mamendéieren duerchgefouert, déi tëscht 2018 an 2023 op dräi Plazen a Sierra Leone gefaange goufen. D'Studie hat zum Zil, d'viral Diversitéit ze charakteriséieren, Kandidaten mat engem Aarteiwwerdroungspotenzial z'identifizéieren, de zoonotesche Risiko ze evaluéieren a Beweiser ze generéieren fir Frühwarnsystemer fir nei infektiéis Krankheeten z'ënnerstëtzen.
Kärmethoden
D'Studie huet e komplette Workflow fir viral Metagenomik ugewannt:
- Proufveraarbechtung:Häerz-, Liewer-, Mëlz-, Longen- a Nierengewebe goufen gesammelt, zesummegefaasst, homogeniséiert an enger totaler RNA-Extraktioun ënnerworf.
- Sequenzéierung an Assembléierung:D'Depletioun vun der ribosomaler RNA gouf virum Opbau vun der Bibliothéik duerchgefouert, gefollegt vun enger High-Throughput-Sequenzéierung mat der Illumina NovaSeq 6000 Plattform. Viral Contigs goufen de novo zesummegesat.
- Virusidentifikatioun:Viren goufen op Basis vun der RNA-ofhängeger RNA-Polymerase (RdRp) Genausriichtung identifizéiert. Nëmme Wierbeldéier-assoziéiert Viren goufen zréckbehalen, ausser Bakterien-, Pilz- a Planzeviren.
- Bioinformatesch Analyse:Phylogenetesch Rekonstruktioun, Rekombinatiounsanalyse, Modelléierung vum Iwwerdroungsnetz iwwer verschidde Spezies an eng zoonotesch Risikobewertung goufen duerchgefouert.
- Serologesch Validatioun:E VSV-baséierte Pseudovirus-Neutralisatiounsassay gouf fir de Bat-ledantevirus 2 entwéckelt. Neutraliséierend Antikörper goufen an 2,8% vun de mënschleche Serum nogewisen, wat Hiweiser op eng potenziell zoonotesch Iwwerdroung liwwert.
StudéierenResultater
1. Viral Entdeckung a Diversitéit
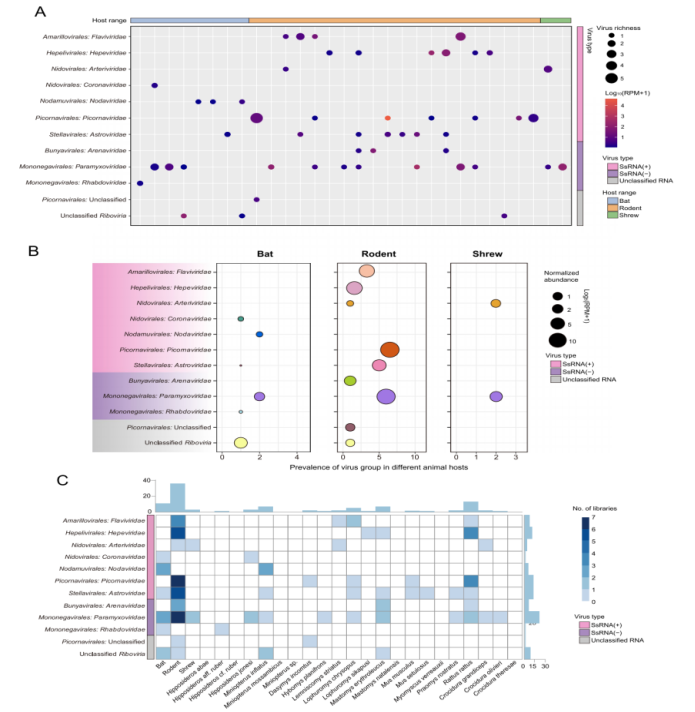
Dës Studie huet eng transkriptomesch Sequenzéierungsanalyse op 846 wëll Déieren duerchgefouert, déi a Sierra Leone gesammelt goufen, dorënner Nager, Fliedermais a Spëtzmais. Baséierend op komplette RNA-ofhängegen RNA-Polymerase (RdRp) Gensequenzen goufen insgesamt 39 Mamendéieren-assoziéiert RNA-Viren identifizéiert, dorënner 13 virdru bekannte Viren an 26 nei Viren.
Wat d'Viruszesummesetzung ugeet, huet d'Famill Paramyxoviridae déi héchst Diversitéit an allen dräi Wirtsuerdnungen opgewisen, gefollegt vun Astroviridae a Picornaviridae. Wat d'Verdeelung vum Wirt ugeet, hunn d'Nager déi gréisst viral Diversitéit bäigedroen, mat insgesamt 26 Virusarten, wat op hir prominent Roll als Reservoir vun der viraler Diversitéit an der Regioun hiweist.
2. Zoonotescht Risiko
D'Bewäertung vum zoonotische Risiko huet dräi bekannt zoonotesch Viren identifizéiert: Encephalomyokarditisvirus, Lassavirus a Rocahepevirus-Aarten. Zousätzlech goufen dräi Viren - Melianvirus, Rodent-Hepatitisvirus an Hunnivirus A - als e potenziellen Spillover-Risiko identifizéiert.
Vun den 26 nei entdeckte Viren gouf vu véier op Basis vu phylogeneteschen a genomesche Charakteristiken e groussen zoonotesche Potenzial virausgesot. Besonnesch de Bat ledantevirus 2 huet déi nootste phylogenetesch Verwandtschaft mam bekannte Le Dantec-Virus gewisen, deen de Mënsch infizéiert.
Spéider serologesch Ënnersichunge hunn dës Erkenntnis weider ënnerstëtzt, well neutraliséierend Antikörper géint de Bat ledantevirus 2 an 2,8% vun de Sera vun Awunner aus der Géigend nogewise goufen. Dëst Resultat weist drop hin, datt net erkannt oder asymptomatesch Infektiounen an der mënschlecher Populatioun scho virkomm sinn, wat e potenziellen, awer virdru net erkannten, zoonoteschen Iwwerdroungswee ervirhieft.
3. Dynamik vun der Iwwerdroung iwwer verschidde Spezies
D'Analyse vun der Iwwerdroung tëscht verschiddene Spezies huet gewisen, datt Nager eng zentral Positioun am Virusdeelnetz anhuelen, andeems se als Schlësselknueten handelen, déi den Austausch vu Viren tëscht den Aarte vum Wirt erliichteren. Insgesamt goufen 15 Viren identifizéiert, déi de Potenzial fir eng Iwwerdroung tëscht verschiddene Spezies hunn.
Weider Analysen vun den Iwwerdroungsmuster tëscht verschiddenen Uerder weisen drop hin, datt d'Deele vu virale Krankheeten méi dacks tëscht Wirten an der selwechter taxonomescher Uerdnung stattfonnt huet, wat drop hiweist, datt d'Verwandtschaft tëscht de Wirten eng wichteg Roll an der Iwwerdroungsdynamik spillt. Am Géigesaz dozou hunn d'Fliedermais eng relativ méi niddreg Kapazitéit fir d'Iwwerdroung tëscht verschiddenen Uerder gewisen.
Wichteg ass, datt bei bestëmmte Virussen Unzeeche vun enger Erweiderung vum Wirtsberäich observéiert goufen. Zum Beispill gouf de Melian-Virus, deen virdru als spezifesch fir Spëtzmais ugesi gouf, an dëser Studie och bei Nager nogewise, wat op eng potenziell Verännerung vun der Adaptabilitéit vum Wirt an e erhéicht Risiko fir eng méi breet Iwwerdroung hiweist.
Conclusiounen an Auswierkunge fir d'ëffentlech Gesondheet
- Héich Viromdiversitéit bei wëlle klenge Säugetieren:D'Entdeckung vun 39 RNA-Viren, dorënner 26 nei Aarten, weist e grousse Virusreservoir an der Regioun op a bericht fir d'éischt Kéier iwwer nei Viren mat héijem zoonotesche Potenzial (z.B. Bat ledantevirus 2).
- Nager als prioritär Iwwerwaachungsziler:Nager handelen als Schlësselzentren fir d'Virusiwwerdroung a droen déi héchst viral Diversitéit, wat de gréisste Spillover-Risiko duerstellt.
- Bedierfnes fir integréiert Iwwerwaachungsstrategien:D'Resultater ënnerstëtzen d'Prioritéit fir Nager an aktive Iwwerwaachungsprogrammer an d'Ëmsetzung vun integréierten Approchen, déi Metagenomik, Serologie an ekologesch Iwwerwaachung op de Schnëttplazen tëscht Mënsch a Wëld kombinéieren.
Insgesamt liwwert dës Studie wichteg Beweiser fir Frühwarnsystemer a Risikobewäertungsrahmen fir opkomende zoonotesch Krankheeten z'ënnerstëtzen, wat d'Wichtegkeet vun enger proaktiver Iwwerwaachung an Héichrisikoregiounen ënnersträicht.
Produktinformatiounen
Zäitpunkt vun der Verëffentlechung: 23. Mäerz 2026